Nat. Methods | 利用单一深度学习模型整合多碎裂策略,提高LC-MS蛋白质组检测覆盖度
Nat. Methods | 利用单一深度学习模型整合多碎裂策略,提高LC-MS蛋白质组检测覆盖度

DrugAI
发布于 2026-03-30 18:50:42
发布于 2026-03-30 18:50:42
DRUGONE
在基于液相色谱-质谱联用(LC-MS)的蛋白质组学研究中,碎裂方式直接影响肽段鉴定的数量和质量。不同碎裂技术能够提供互补信息,但在实际实验中往往需要分别采集和分析,导致流程复杂且难以整合。研究人员提出一种基于深度学习的统一模型,使不同碎裂模式产生的谱图能够在同一分析框架中进行预测和匹配,从而在不改变标准LC-MS流程的情况下提升蛋白质组覆盖率。
该模型能够同时学习多种碎裂机制下的谱图特征,并用于预测不同实验条件下的碎片分布,使得传统数据库搜索可以直接利用多碎裂信息。研究结果表明,将替代碎裂技术整合到标准工作流程中,可显著增加可鉴定肽段和蛋白数量,并提高低丰度蛋白的检测能力。该方法为高通量蛋白质组学提供了一种无需额外实验复杂度即可提升检测深度的新策略。

在自底向上的蛋白质组学中,肽段经碎裂后产生的MS/MS谱图用于鉴定蛋白序列。常用的碎裂方式包括碰撞诱导碎裂和电子转移碎裂等,不同技术产生的碎片类型不同,因此具有互补性。利用多种碎裂方式可以提高肽段鉴定成功率,并改善翻译后修饰和长肽段的解析能力。
然而,在实际工作流程中,将多种碎裂技术整合到同一次实验中仍然具有挑战。一方面,不同碎裂方式产生的谱图特征差异较大,使数据库搜索难以统一处理;另一方面,建立针对每种碎裂方式的预测模型需要大量数据,并增加计算复杂度。
近年来,深度学习在质谱谱图预测中取得显著进展。通过学习肽段序列与碎片谱之间的关系,模型可以准确预测在特定条件下产生的谱图。研究人员提出,如果能够构建一个能够同时处理多种碎裂机制的统一模型,就可以在不改变实验流程的情况下整合不同碎裂信息,从而提高蛋白质组检测深度。
方法
研究人员开发了一种深度学习模型,用于同时预测多种碎裂方式下的MS/MS谱图。模型以肽段序列为输入,并结合实验条件信息预测不同碎裂模式产生的离子强度分布。通过在包含多种碎裂技术的数据集上进行训练,模型能够学习不同碎裂机制之间的共同规律。
在实际分析中,该模型用于生成理论谱图,并将这些预测结果用于数据库搜索,从而使搜索算法能够同时匹配多种碎裂模式产生的谱图。这样可以在不改变标准LC-MS实验流程的情况下,利用替代碎裂技术提供的额外信息。
研究人员还将该模型集成到现有蛋白质组分析软件中,使其可以在常规数据处理流程中直接使用,从而降低应用门槛。
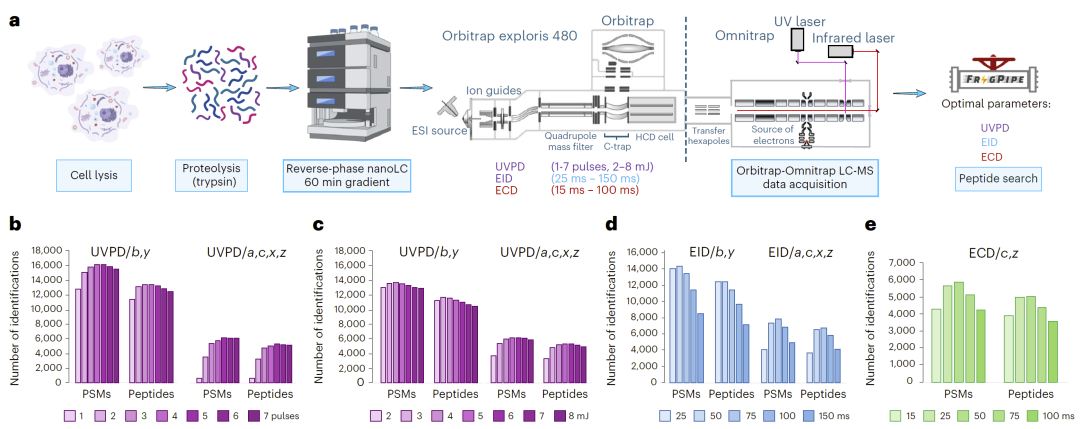
图1: 自底向上蛋白质组实验中ECD、EID和UVPD参数的优化。
结果
研究人员首先评估该模型在谱图预测任务中的准确性。结果显示,模型能够同时准确预测多种碎裂模式下的谱图,并且预测精度与针对单一碎裂方式训练的模型相当。这表明统一模型能够有效捕捉不同碎裂机制的共同特征。
随后,研究人员将该模型应用于真实蛋白质组数据分析。通过将替代碎裂方式整合到标准LC-MS流程中,鉴定到的肽段数量明显增加,特别是在复杂样品中,检测到更多低丰度蛋白。
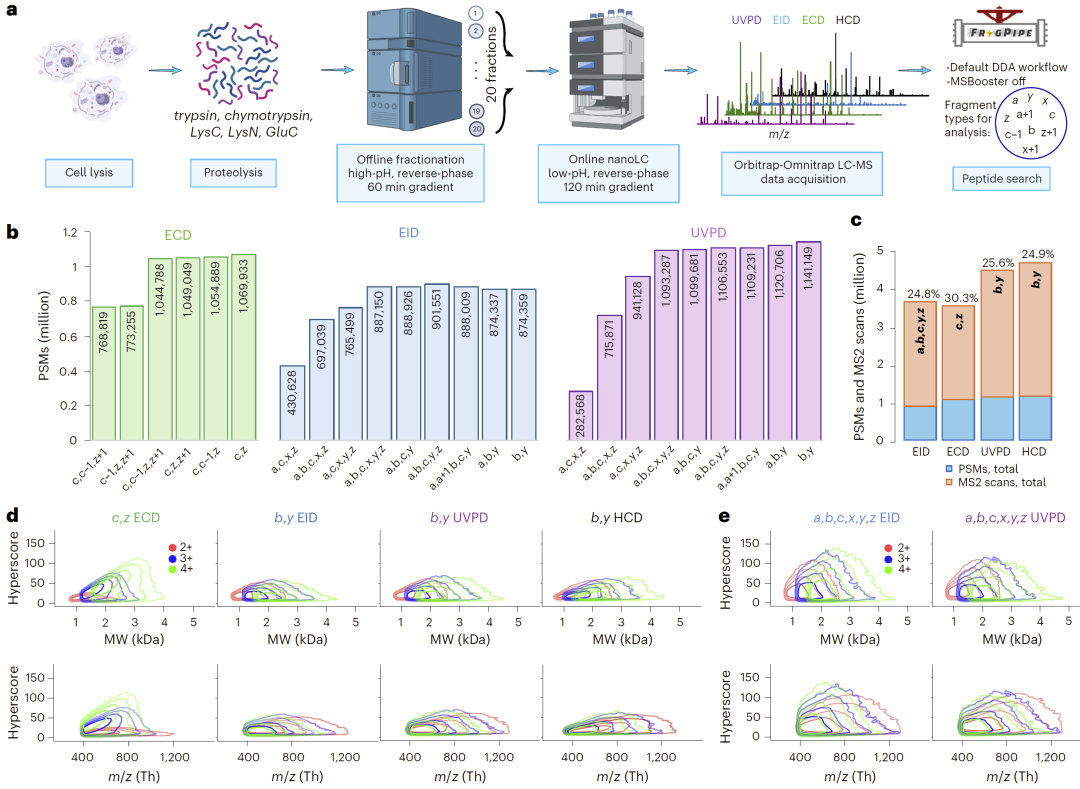
图2: 大规模自底向上ECD、EID、UVPD和HCD碎裂数据分析。
进一步分析发现,多碎裂模式提供的互补信息能够显著提高谱图匹配置信度。对于传统方法难以识别的肽段,结合多碎裂预测后可以成功鉴定,从而提高整体蛋白质组覆盖率。
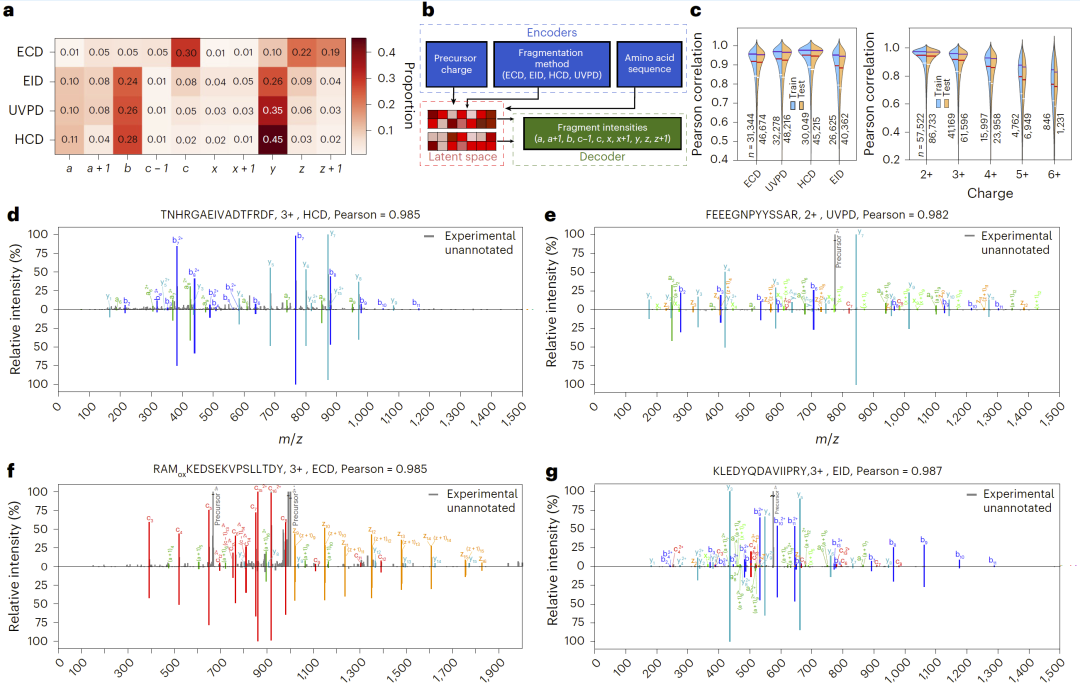
图3:深度学习训练流程:从谱图标注到模型评估。
研究人员还测试了该方法在不同样品类型中的表现,包括细胞裂解物和复杂生物样本。结果表明,该模型在各种条件下均能稳定提高鉴定数量,并且不会显著增加误识别率。
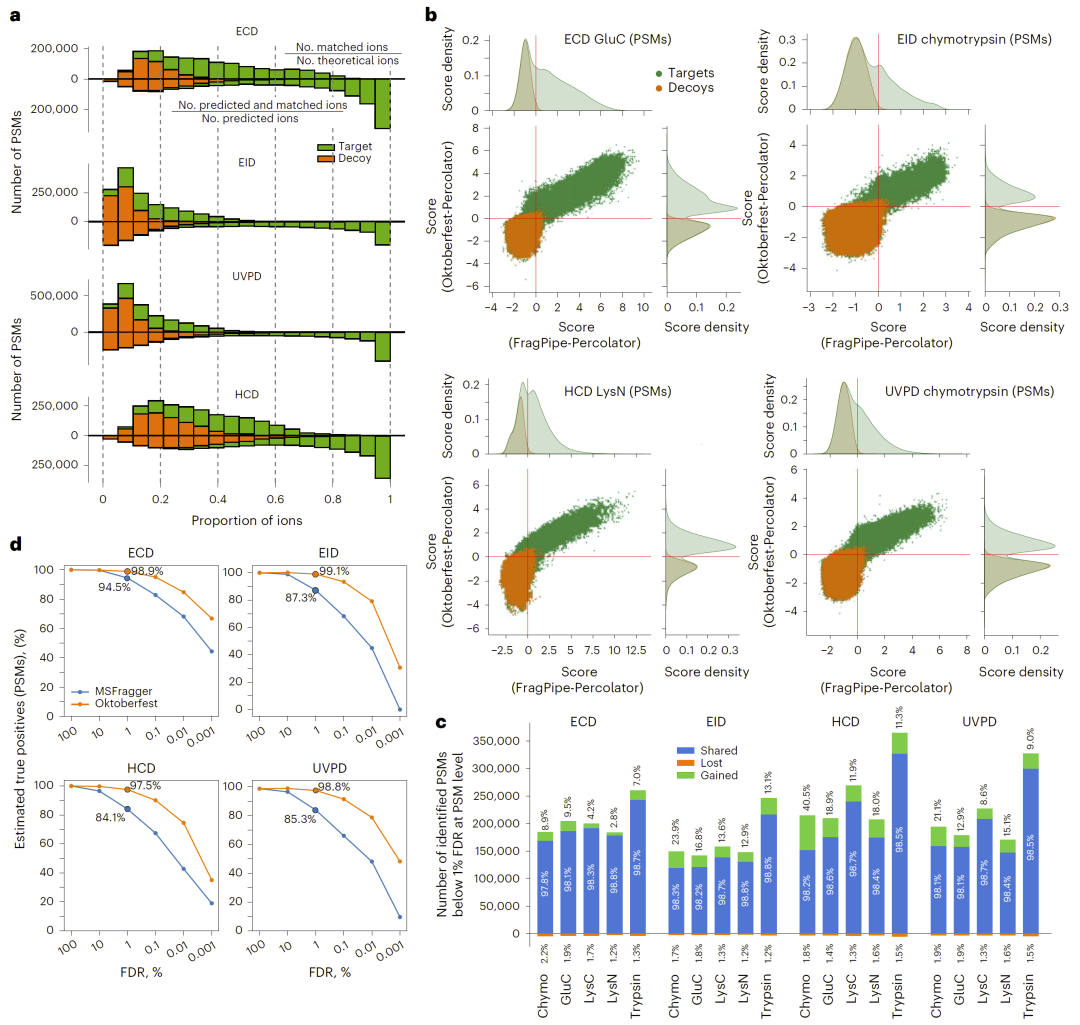
图4:强度预测提升ECD、EID、HCD和UVPD数据的数据库搜索质量。
为了评估该方法在大规模实验中的应用潜力,研究人员进行了长时间梯度和高通量测定实验。结果显示,在保持实验时间不变的情况下,整合替代碎裂技术能够持续增加可鉴定蛋白数量,并改善翻译后修饰肽段的检测。
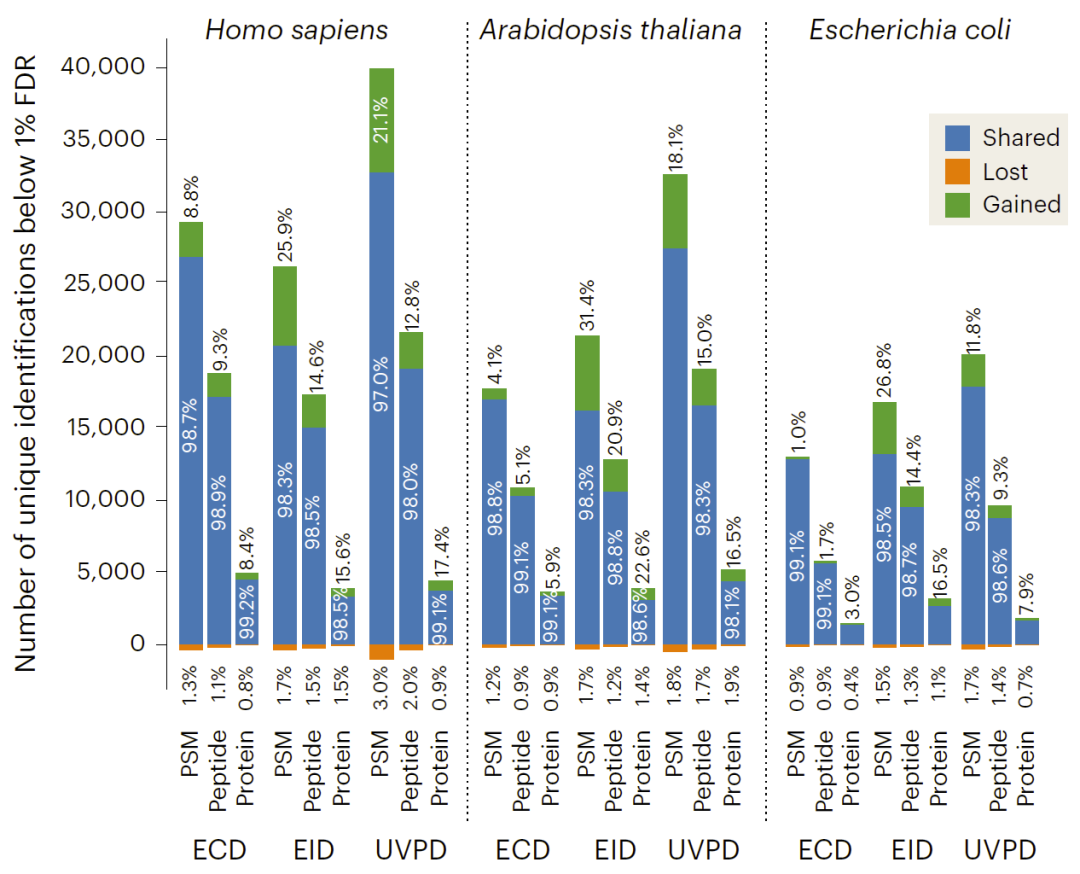
图5:强度预测提升ECD、EID和UVPD的DIA数据搜索质量。
讨论
本研究提出了一种统一的深度学习模型,使多种碎裂技术能够在同一LC-MS分析流程中协同使用,从而显著提高蛋白质组检测深度。该方法避免了为不同碎裂方式分别建立模型的复杂过程,并使替代碎裂技术可以直接应用于常规实验。
研究人员认为,利用深度学习进行谱图预测是实现高覆盖率蛋白质组学的重要方向。通过统一模型整合不同实验信息,可以在不增加实验成本的情况下获得更多鉴定结果。
未来,该方法有望进一步扩展到更多碎裂技术和更多实验条件,并结合更大规模数据训练更强大的模型,从而推动蛋白质组学向更高灵敏度和更高通量发展。
整理 | DrugOne团队
参考资料
Levin, N., Saylan, C.C., Lapin, J. et al. Integration of alternative fragmentation techniques into standard LC-MS workflows using a single deep learning model enhances proteome coverage. Nat Methods (2026).
https://doi.org/10.1038/s41592-026-03042-9

内容为【DrugOne】公众号原创|转载请注明来源
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2026-03-23,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读

