超级增强子系列文章13:Deeptools绘制超级增强子区域组蛋白或转录因子富集热图
超级增强子系列文章13:Deeptools绘制超级增强子区域组蛋白或转录因子富集热图
三兔测序学社
发布于 2026-04-13 11:28:36
发布于 2026-04-13 11:28:36
1.图片解读
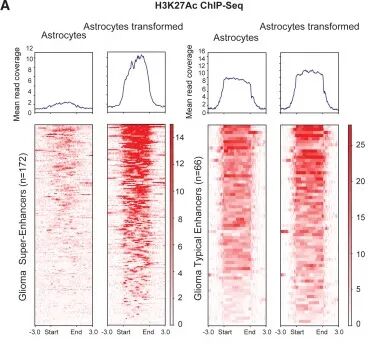
1.1、图表核心信息 这是一张H3K27Ac ChIP-Seq的富集热图与平均信号曲线图,用于比较正常星形胶质细胞(Astrocytes)和转化型星形胶质细胞(Astrocytes transformed)在超级增强子与普通增强子区域的H3K27ac 组蛋白修饰状态: 左侧:胶质瘤超级增强子(Glioma Super-Enhancers, n=172) 右侧:胶质瘤典型增强子(Glioma Typical Enhancers, n=66) 1.2、图表结构解读 平均信号曲线(上半部分) 横轴:增强子中心上下游 ±3.0 kb 区域 纵轴:Mean read coverage(平均测序读段覆盖度,反映 H3K27Ac 平均富集水平) 对比结果: 超级增强子:正常细胞几乎无明显富集峰,转化型细胞在中心区域形成尖锐的高富集峰。 典型增强子:正常细胞已有明显富集峰,转化型细胞的峰更高、更宽,说明整体激活水平进一步提升。
热图部分(下半部分) 每一行代表一个增强子区域,列是增强子中心(Start-End)上下游 ±3.0 kb 的基因组坐标。 颜色深浅代表H3K27Ac 信号强度(红色越深,信号越强)。 对比两组细胞: 超级增强子:转化型星形胶质细胞的红色信号显著强于正常星形胶质细胞,且在超级增强子中心区域形成明显的高富集峰。 典型增强子:两组均有较强信号,但转化型星形胶质细胞的富集程度仍略高于正常细胞。
1.3、生物学意义解读 H3K27Ac 是活跃增强子 / 启动子的组蛋白修饰标记,信号强弱直接反映区域的增强子激活程度。 超级增强子(Super-Enhancers):通常调控关键细胞身份基因和癌基因,在肿瘤发生中常被异常激活。本图显示:转化后的星形胶质细胞中,胶质瘤超级增强子被显著激活,而正常细胞中这些区域几乎沉默。 典型增强子(Typical Enhancers):调控一般功能基因,本图显示其在正常细胞中已有基础活性,转化后活性进一步增强。 核心结论:星形胶质细胞恶性转化过程中,胶质瘤相关增强子(尤其是超级增强子)被大范围激活,可能通过上调癌基因表达推动肿瘤发生。
2.Deeptools 用法
# 计算矩阵:
computeMatrix scale-regions \
-S H3K27ac-CHIP.bw \
-R SE.bed TE.bed \
--binSize 10 \
--skipZeros\
--regionBodyLength 5000 \
-b 3000 -a 3000 \
-o SE_TEmatrix.gz
# 绘制热图:对应图片输出
plotHeatmap -m SE_TEmatrix.gz -out SETEHeatmap.pdf 3.代码解读
这段代码使用Deeptools的computeMatrix在scale-regions模式下计算基因组区域的信号矩阵,并通过plotHeatmap生成热图可视化,用于分析组蛋白修饰(H3K27ac)和蛋白(BRD4)在超级增强子(SE)和典型增强子(TE)区域的信号分布。以下是详细解读:
3.1. computeMatrix scale-regions命令解读 scale-regions模式:将所有输入区域(如增强子)缩放至--regionBodyLength指定的长度(此处5000 bp),并在其上下游延伸指定距离,适用于分析可变长度区域 。 -S H3K27ac-CHIP.bw 输入bigWig文件,包含H3K27ac ChIP-seq信号数据 。 -R SE.bed TE.bed:指定BED格式的区域文件,分别对应超级增强子(SE)和典型增强子(TE),多个文件会分组处理 。 --binSize 10:将每个区域划分为10 bp的窗口,计算每个窗口的平均信号值,提高分辨率 。 --skipZeros:跳过所有信号值为0的窗口,减少输出文件大小并避免噪声干扰 。 --regionBodyLength 5000:关键参数,将所有区域缩放至5000 bp的统一长度,确保信号在可比尺度上计算 。 -a 3000 -b 3000:在缩放区域的下游(-a)和上游(-b)各延伸3 kb,总覆盖区域为“上游3kb + 缩放体5000 bp + 下游3 kb”。 -o SE_TEmatrix.gz:输出gzip压缩的矩阵文件(SE_TEmatrix.gz),供后续可视化工具使用 。
3.2. plotHeatmap命令解读 此命令基于computeMatrix生成的矩阵文件创建热图,参数如下: -m SE_TEmatrix.mat.gz:输入矩阵文件(由computeMatrix生成),包含SE和TE区域的信号强度数据 。 -out SETEHeatmap.pdf:输出PDF格式的热图文件(SETEHeatmap.pdf),文件后缀自动决定格式 。 未显式参数: 默认行为:热图按信号强度自动排序,区域组(SE/TE)和样本(H3K27ac)分开展示 。 可扩展选项:如需调整颜色(--colorMap)或添加聚类(--kmeans),需额外指定 。
3.3. 整体流程与注意事项 流程逻辑:通过computeMatrix提取信号并生成矩阵。用plotHeatmap将矩阵转换为热图,直观展示信号富集模式 。 注意事项:区域缩放:scale-regions模式适合基因体等长度不一的区域,若需固定参考点(如TSS),应改用reference-point模式 。 文件一致性:plotHeatmap的输入文件名需与computeMatrix输出完全匹配(此处应为SE_TEmatrix.gz,代码中误写为.mat.gz,可能导致报错)。 可视化优化:建议添加--samplesLabel和--regionsLabel以标注样本和区域组,提升可读性 。
4.参考文档
图片来源:Primary Source: Deforzh, E., Kharel, P., Zhang, Y., Karelin, A., El Khayari, A., Ivanov, P., & Krichevsky, A. M. (2024). "HOXDeRNA activates a cancerous transcription program and super enhancers via genome-wide binding." Molecular Cell, 84(20), 3950–3966.e6. DOI: 10.1016/j.molcel.2024.09.018
Deeptools官方文档:https://deeptools.readthedocs.io/en/latest/content/tools/plotHeatmap.html
Deeptools中文博客文章:https://cloud.tencent.com/developer/article/1556577
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2026-03-31,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读
目录

