脚本扩展--空间邻近性分析
原创脚本扩展--空间邻近性分析
原创
追风少年i
发布于 2026-04-02 10:05:44
发布于 2026-04-02 10:05:44
作者,Evil Genius
今天我们扩展脚本,大家应该经常在文章中看到这样的分析结果。
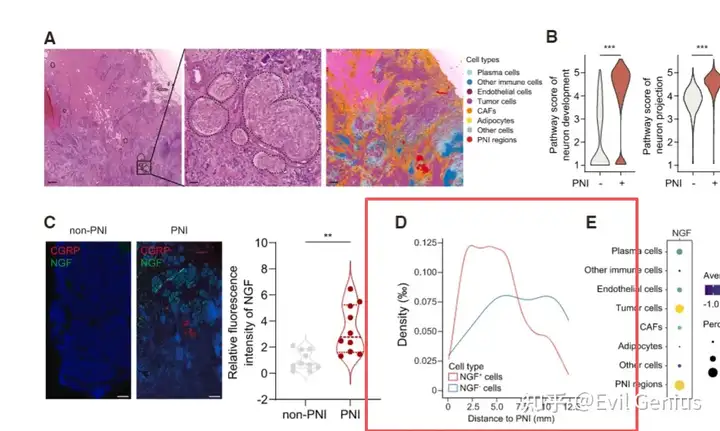
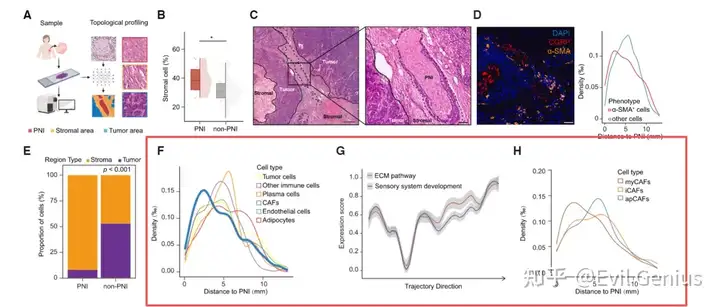
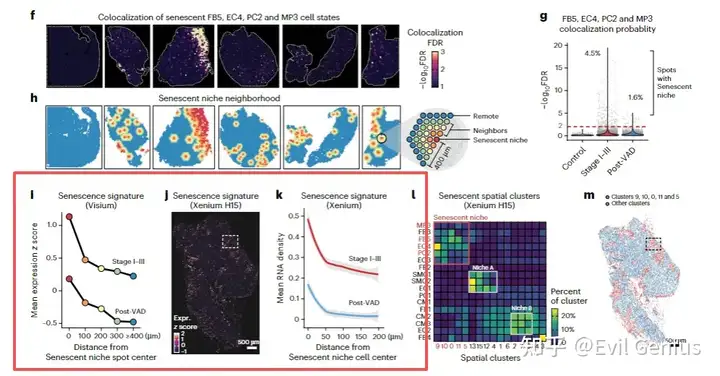
一般来讲,很多人立马想到用squidpy来分析

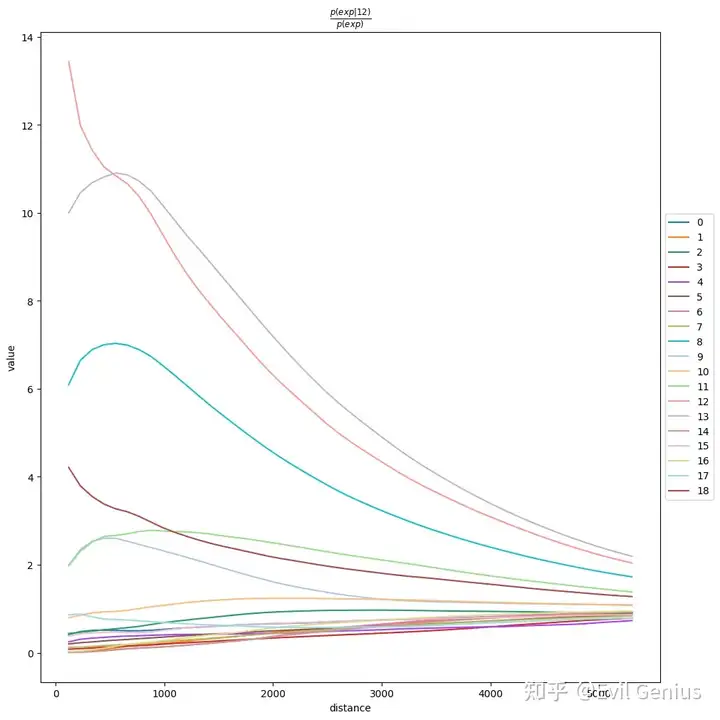
Squidpy的共现概率分析是一种描述性统计方法。它通过比较局部条件概率和全局背景概率,提供了一个直观的指标来判断不同细胞类型在空间上是相互吸引、排斥还是随机分布。这有助于我们从空间组织中挖掘细胞间潜在的通讯或生态位关系。
但是这个方法不够完美,实际操作中不能完全满足分析的需求,我们希望的是,分距离阶段看细胞的丰度变化。
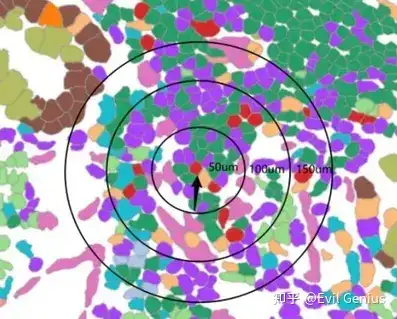
即0-20um范围内,细胞的含量组成,20-40um的含量组成,以此类推,一般推到200um,然后看细胞比例的整体变化,这个过程不能累计,而是每段距离单独计算,然后拟合,我们换一个方法实现。
library(tidyverse)
library(phenoptr)
csd <- “读取示例数据”
csd %>% count(Phenotype)
distances <- find_nearest_distance(csd)
glimpse(distances)
csd_with_distance <- bind_cols(csd, distances)
merged_with_distance <- merged %>%
group_by(`Sample Name`) %>%
do(bind_cols(., find_nearest_distance(.)))
csd_with_distance %>% group_by(Phenotype) %>%
select(Phenotype, starts_with('Distance to')) %>%
summarize_all(~round(mean(.), 1))
ggplot(csd_with_distance, aes(`Distance to CD8+`, color=Phenotype)) +
geom_density(size=1)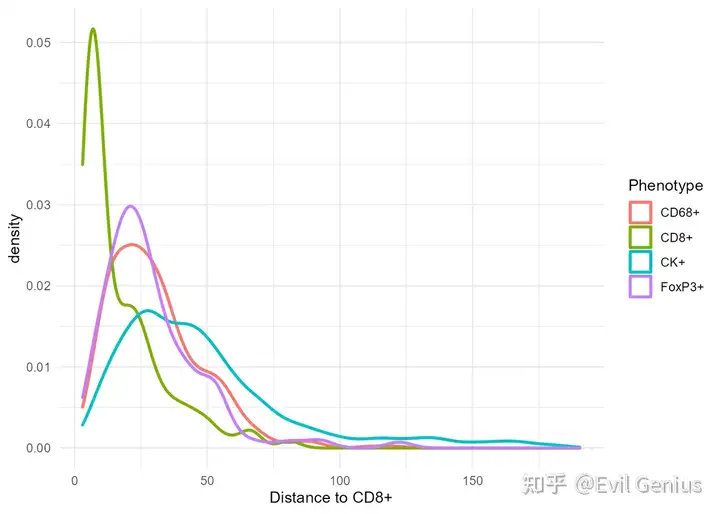
# Filter to just CD8+ and CK+ cells
cd8_cells = csd_with_distance %>% filter(select_rows(csd_with_distance, 'CD8+'))
ck_cells = csd_with_distance %>% filter(select_rows(csd_with_distance, 'CK+'))
# For each CD8+ cell, join with the data for the nearest CK+ cell
cd8_to_ck = cd8_cells %>% left_join(ck_cells, by=c('Cell ID CK+'='Cell ID'),
suffix=c('', '.CK'))
# Read a background image and make a base plot
background_path =
system.file("extdata/sample/Set4_1-6plex_[16142,55840]_composite_image.jpg", package='phenoptr')
background = jpeg::readJPEG(background_path) %>% as.raster()
xlim = c(0, 934)
ylim = c(0, 700)
base_plot = ggplot(mapping=aes(`Cell X Position`, `Cell Y Position`)) %>%
phenoptr:::add_scales_and_background(background, xlim, ylim, scale_color='white') +
labs(x='Cell X Position', y='Cell Y Position') +
scale_color_manual('Phenotype', values=c('CD8+'='red', 'CK+'='cyan2'))
# Add lines and points
base_plot + geom_segment(data=cd8_to_ck,
aes(xend=`Cell X Position.CK`, yend=`Cell Y Position.CK`),
color='white') +
geom_point(data=ck_cells, aes(color='CK+'), size=1) +
geom_point(data=cd8_cells, aes(color='CD8+'), size=1) +
labs(title='Nearest CK+ to each CD8+')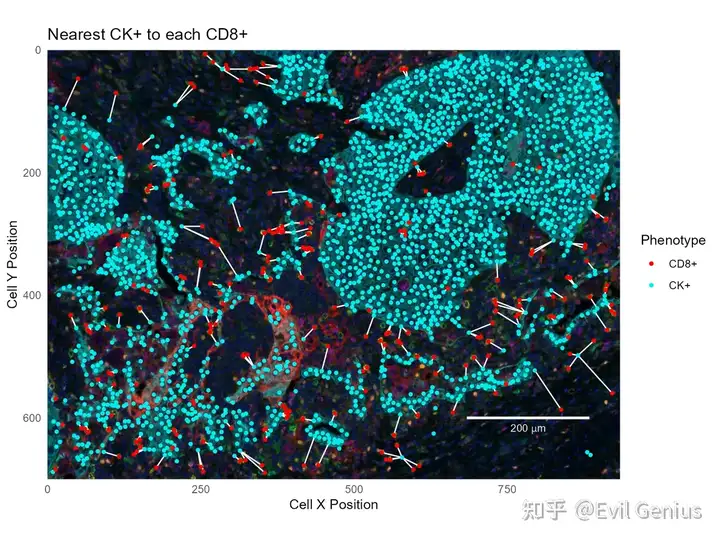
ck_to_cd8 = ck_cells %>% left_join(cd8_cells, by=c('Cell ID CD8+'='Cell ID'),
suffix=c('', '.CD8'))
base_plot +
geom_segment(data=ck_to_cd8,
aes(xend=`Cell X Position.CD8`, yend=`Cell Y Position.CD8`),
color='white') +
geom_point(data=ck_cells, aes(color='CK+'), size=1) +
geom_point(data=cd8_cells, aes(color='CD8+'), size=1) +
labs(title='Nearest CD8+ to each CK+')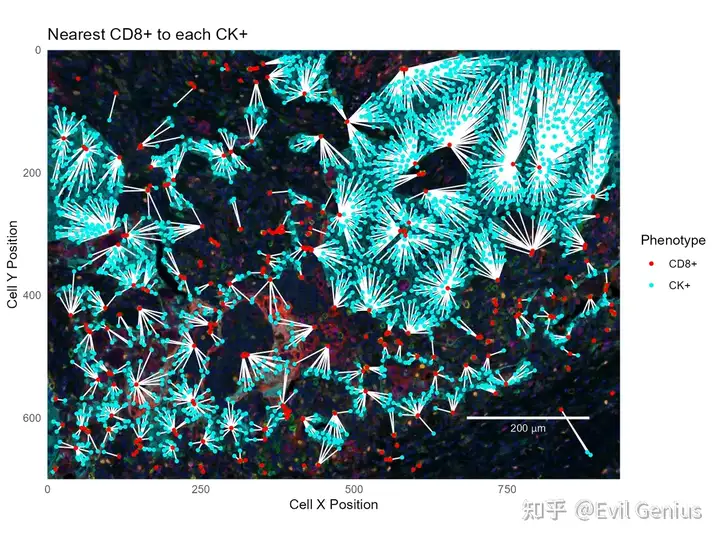
mutual = ck_to_cd8 %>% filter(`Cell ID`==`Cell ID CK+.CD8`)
base_plot +
geom_segment(data=mutual,
aes(xend=`Cell X Position.CD8`, yend=`Cell Y Position.CD8`),
size=1, color='white') +
geom_point(data=ck_cells, aes(color='CK+'), size=1) +
geom_point(data=cd8_cells, aes(color='CD8+'), size=1) +
labs(title='Mutual nearest neighbors - CD8+ and CK+')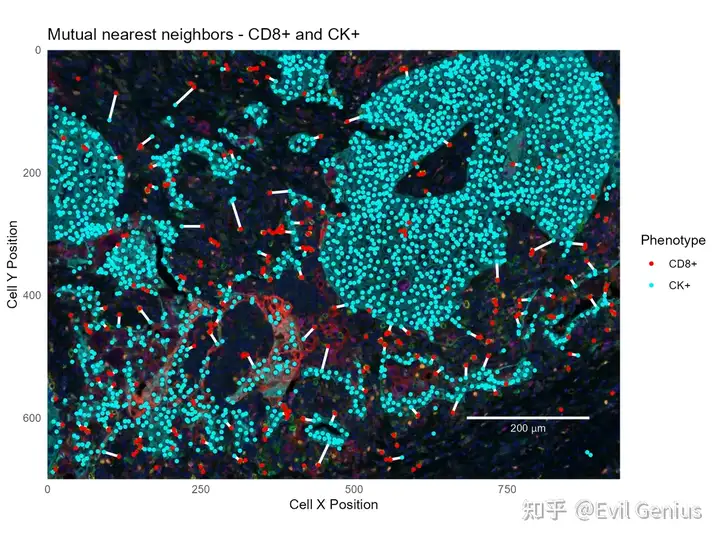
生活很好,有你更好。
原创声明:本文系作者授权腾讯云开发者社区发表,未经许可,不得转载。
如有侵权,请联系 cloudcommunity@tencent.com 删除。
原创声明:本文系作者授权腾讯云开发者社区发表,未经许可,不得转载。
如有侵权,请联系 cloudcommunity@tencent.com 删除。
评论
登录后参与评论
推荐阅读
目录

