AI模型知道Seurat包AggregateExpression/AverageExpression的这个小坑吗?
AI模型知道Seurat包AggregateExpression/AverageExpression的这个小坑吗?

KS科研分享与服务-TS的美梦
发布于 2026-04-02 13:07:59
发布于 2026-04-02 13:07:59
以前还真没有注意,主要是没有遇到上,使用Seurat包AggregateExpression/AverageExpression函数计算基因平均表达量的时候,发现celltype如果有一些特殊字符会发生改变。比如这里遇到的"_"变成"-",一般没有问题,但是在某些情况的使用下会有问题,主要是因为celltype名称不匹配的问题。如果不知道会导致让人摸不着头脑!
unique(scRNA_Y16$celltype)
#[1] MC Astro LAMA IN_SST OPC PN_CUX IN_VIP ODC PN_RO IN_ID IN_PV LAMPs
#Levels: Astro ODC MC OPC PN_CUX IN_SST IN_VIP LAMA IN_ID IN_PV PN_RO LAMPs Vasexp = AggregateExpression(scRNA_Y16,
features = c("NRXN2" , "DSCAM" , "NRXN3" , "GABBR2" , "ROBO2"),
assays = 'RNA')
exp = as.data.frame(exp$RNA)colnames(exp)
#[1] "Astro" "ODC" "MC" "OPC" "PN-CUX" "IN-SST" "IN-VIP" "LAMA" "IN-ID" "IN-PV" "PN-RO"
#[12] "LAMPs" 其实一开始还真想不到是AggregateExpression/AverageExpression的问题,然后查询之后才知道(https://github.com/satijalab/seurat/issues/7893),但是在最新的seurat中会出现warning,提示您这个信息,如果之前的版本不提示那真的是抓耳挠腮!
exp = AverageExpression(scRNA_Y16,
features = c("NRXN2" , "DSCAM" , "NRXN3" , "GABBR2" , "ROBO2"),
group.by = 'celltype',layer = 'data',assays = 'RNA')
#Ahis message is displayed once per session.
#Names of identity class contain underscores ('_'), replacing with dashes ('-')那么我们看看AI知不知道这个事呢?把我们的项目直接塞进去询问,它很明显找不到问题!
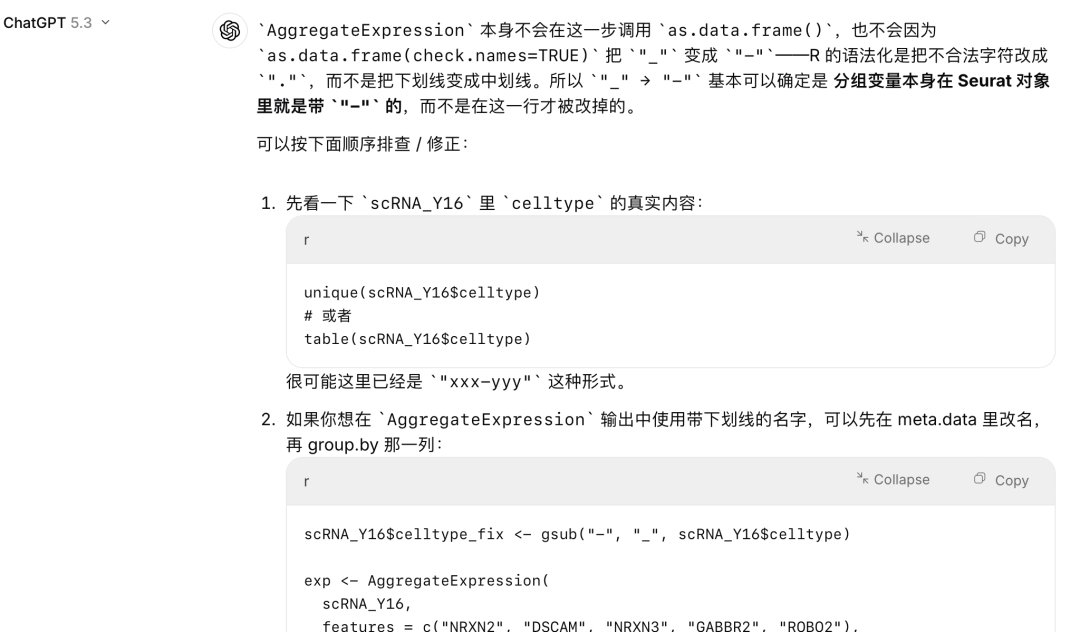
在自检出这一步骤的问题之后,在此针对性提问,就好很多:

一个可能后续不再遇到的小问题,希望大家知晓。那么至于AI,想说的是如果您不了解项目,不了解过程,仅仅依赖AI那么也很难达到目的。我们一直强调AI是辅助,是弥补我们的不足,而不是完全交给它!
觉得分享有用的点个赞再走呗!
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2026-03-24,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读

